Главный приз — Полный геном.

Ранее мы уже делились полезной информацией и ссылками, которые могут пригодиться для работы с биоинформатическими данными. Советуем сначала прочитать предыдущие статьи, если вы их пропустили:
Что такое Полный геном и зачем он нужен
Задача №1. Узнайте пол и степень родства.
Задача №2. Определение популяционной структуры
Дисклеймер
Работа с генетическими данными проводится на Unix системах (Linux, macOS), так как некоторые команды и ПО недоступны на Windows. Поэтому для пользователей Windows одним из самых простых решений будет арендовать виртуальную машину с Linux.
Все описанные ниже операции выполняются в командной строке — терминале. Перед началом выполнения узнайте, как работать в терминале под управлением вашей ОС и использовать команды, так как некоторые из них могут потенциально навредить ОС и вашим данным.
Необходимое ПО
Мы собрали образ виртуальной машины (ВМ) со всем необходимым ПО на Яндекс.Облаке. Инструкции по настройке ВМ и установке ПО можно найти в статье с первой задачей. Там же есть инструкция, как настроить машину, чтобы пользоваться ею бесплатно до 31 декабря 2019 года.
В этой задаче нужно сконвертировать данные генотипирования из формата VCF в формат 23andMe, загрузить полученные файлы в сервис Promethease и ознакомиться с содержимым отчета для каждого образца.
Формат 23andMe представляет собой текстовый формат хранения данных генотипирования и содержит 4 поля, разделенных табуляцией. Первое поле содержит идентификатор вариации (например, rsID), второе — хромосому (допустимые значения этого поля 1-22, Х, Y и MT), третье — позицию на хромосоме, четвертое — генотип (диплоидный при наличии двух гомологичных хромосом, гаплоидный в других случаях). Этот формат поддерживается многими сервисами интерпретации, поэтому в задаче мы будем работать именно с ним.
Для выполнения задачи понадобится программный пакет BCFtools. Если вы его еще не установили, прочитайте статью с первой задачей. В ней содержатся инструкции по установке. Напоминаем, что для участия в новогоднем конкурсе 2019 необходимо выполнение всех задач.
Кроме BCFtools вам понадобится файл create_23andme.sh — bash-скрипт, который используется для генерации данных в формате 23andMe. Этот файл расположен в каталоге /Technical как на Яндекс.Облаке, так и в архиве для скачивания, доступном по ссылке в статье.
Взять на заметку
Существует много сервисов, которые проводят анализ данных генотипирования: MyHeritage, Promethease, FamilyTreeDNA, DNA.LAND, GEDmatch. Они дают загрузить данные генотипирования в различных форматах, зачастую специфичных для конкретного поставщика услуг генотипирования (Ancestry, 23andMe, MyHeritage, FamilyTreeDNA, GenesForGood и т.п.). Наиболее лояльным к формату данных является Promethease: в данный сервис можно загрузить как VCF, так и файлы в формате 23andMe.
Существует несколько проблем совместимости форматов и сервисов:
- Разные компании используют разные версии генома для картирования генетических вариаций.Эта проблема решается так называемым лифтовером (liftover), когда происходит замена позиций генетических вариаций в исходных данных на соответствующие им в другой версии генома. Например, Атлас выдает данные генотипирования по версии генома GRCh38, а GEDmatch принимает данные по предыдущей версии генома GRCh37. Конвертация координат генетических вариаций из GRCh38 в GRCh37 и называется лифтовером.
- Использование уникальных идентификаторов генетических вариаций, отличных от rsIDs. Подобные несовместимости решаются путем исключения подобных записей из файла либо их аннотированием — присвоением идентификатора rsID. Второе возможно не всегда.
- Сервисы используют фиксированный набор генетических вариаций. Иногда несоответствие хотя бы части загружаемых данных приводит к ошибке загрузки. Данная проблема актуальна, например, для MyHeritage. Ее можно решить путем выделения набора идентификаторов генетических вариаций, не вызывающих ошибку загрузки.
Используемые данные
Напоминаем, что в данном руководстве используются специально отобранные нами открытые данные из проекта «1000 Геномов». Для анализа мы выбрали 10 образцов с информацией о генотипах ~85 миллионов вариаций, которые получены путем анализа данных NGS с выравниванием на версию генома GRCh37. Родственные связи и популяции данных образцов указаны на Рисунке 1.
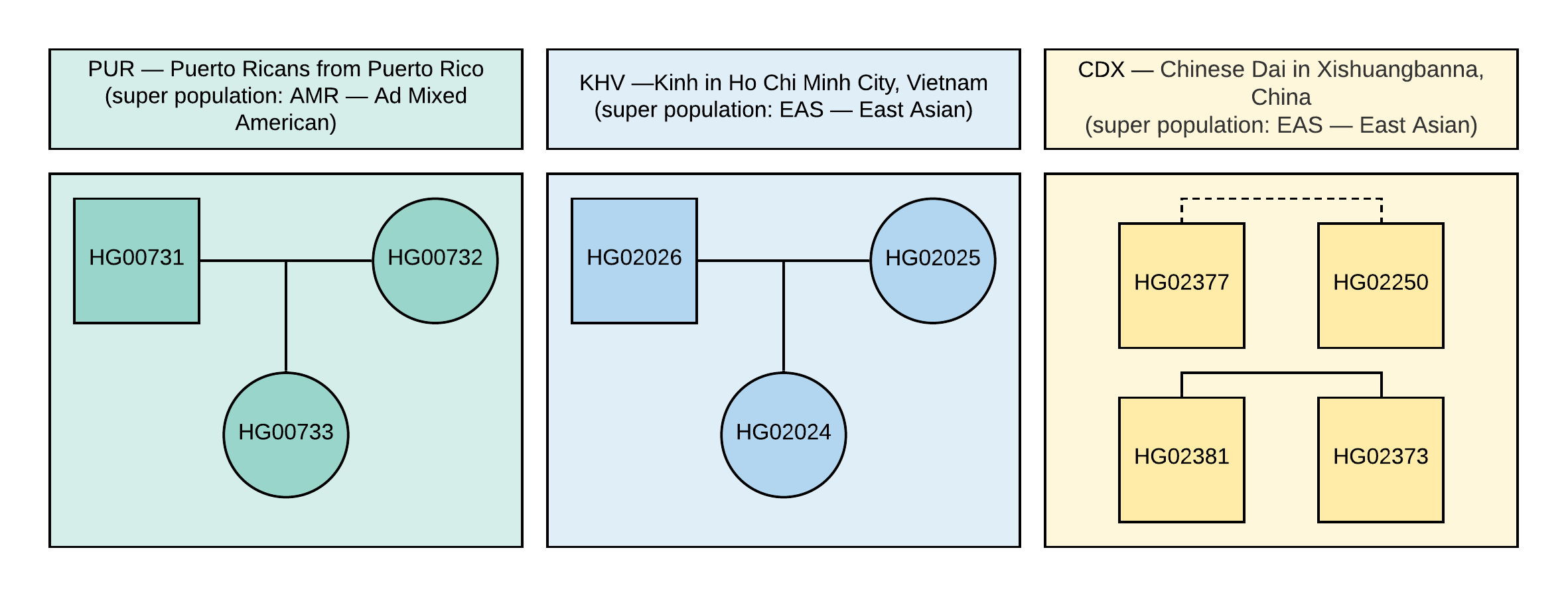
Рисунок 1. Родословная используемых в VCF образцов (квадрат соответствует мужскому полу, круг — женскому). Пунктирная линия соответствует неустановленному родству второго порядка.
Конвертация VCF
Ниже приведены инструкции по конвертации VCF файла и загрузке полученных данных в сервис Promethease, который совсем недавно стал бесплатным. Предлагаем ознакомиться с полученным отчетом Promethease по какому-либо из образцов. Используйте отфильтрованный по списку вариаций VCF файл, полученный в задаче №1.
# перейдите в нужную вам директорию
bcftools query -s HG00731 -f '[%SAMPLE]t%IDt%CHROMt%POSt%REFt%ALTt[%GT]n' -e '%ID=="."' CEI.1kg.2019.demo.subset.vcf.gz | create_23andme.sh > HG00731.subset.23andme.txt
# скачайте на локальный компьютер файл HG00731.subset.23andme.txtКоманда bcftools query позволяет извлекать из VCF файла любую доступную информацию в формате, заданном пользователем после флага -f. Флаг -s указывает на идентификатор образца (HG00731), для которого необходимо извлечь данные. Флаг -е используется для обозначения критерия исключения, в данном случае ’%ID=="."’ исключает записи, в которых нет идентификатора rsID. Выход с bcftools query передается на вход в скрипт create_23andme.sh, который преобразует данные в TSV формат с 4 колонками (rsID, хромосома, позиция, генотип) и записывает их в файл. Можете скачать и сохранить скрипт create_23andme.sh себе для работы с собственными данными полногеномного секвенирования.
Скрипт create_23andme.sh использует извлеченные из VCF файла поля для определения типа генетической вариации (однонуклеотидная вариация SNV, инсерция INS или делеция DEL) и записи идентификатора rsID, хромосомы, позиции и аллелей в stdout в соответствии с определенным типом вариации (A, G, T и С являются допустимыми аллелями для типа SNV, I и D — допустимые обозначения аллелей для типов INS и DEL).
Имейте в виду, что процесс конвертации занимает достаточно много времени: около 4 часов на один файл для одного образца с ~1 миллионом вариаций. Параллелизация BCFtools не поддерживается.
Перейдите на promethease.com и зарегистрируйтесь. Нажмите на кнопку Upload raw data (Рисунок 2) и загрузите файл HG00731.subset.23andme.txt. После окончания загрузки нажмите на кнопку Create free report и введите желаемое название отчета, который будет сформирован по вашим данным. После составления отчета вам придет уведомление на электронную почту и вы сможете ознакомиться с содержимым отчета. Найдите в отчетах для каждого образца группу крови, которую определила система интерпретации Promethease, в системе AB0/Rh (Rh — Резус-фактор). Проверьте полученные вами результаты на соответствие с Таблицей 1.
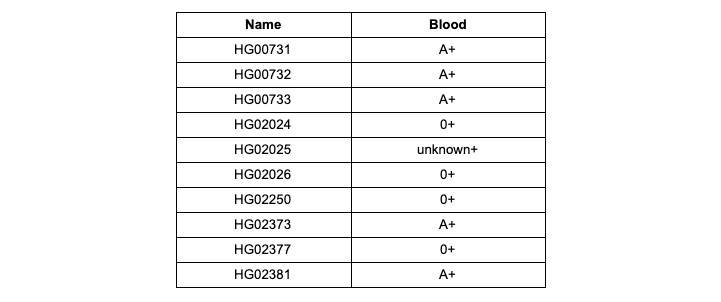
Таблица 1. Группы крови и Резус-фактор, полученные по результатам анализа Promethease образцов из демонстрационного датасета
Атлас использует отличающиеся от Promethease пороги включения того или иного признака в интерпретацию по уровню доказательности. Под уровнем доказательности понимается совокупность результатов статистических тестов и критериев значимости каждой связи, наблюдаемой между генетической вариацией и какой-либо чертой человеческого организма. Множество признаков, которые можно найти в отчете Promethease, имеют низкий уровень доказательности и/или имеют высокий уровень только в ограниченном наборе популяций, например только для представителей азиатской популяции.
external_interpretation_rsids.txt) хранится в отдельном файле в каталоге /Technical, и его можно использовать для фильтрации VCF с последующей конвертацией по аналогии с инструкцией выше. Также этот файл можно использовать для фильтрации данных генотипирования с чипа, чтобы иметь возможность загрузить их на MyHeritage. Если у вас уже есть приобретенный генетический тест «Атлас», вы можете выгрузить данные генотипирования в формате из личного кабинета и отфильтровать их по предложенному списку вариаций — первая колонка в выгружаемых из личного кабинета данных.
Отметим, что используемые в данном руководстве файлы всегда содержат заполненное поле ALT (альтернативный аллель), что позволяет понять, к какому типу относится каждая из вариаций (INS, DEL, SNV) и правильно создать запись в формате 23andMe. Данные полногеномного секвенирования в Атлас содержат заполненный ALT аллель только в тех местах, где этот аллель был обнаружен, в противном случае информации для заполнения поля ALT при генерации VCF файла просто не существует. Выдача данных по гомозиготным референсным сайтам (позициям в геноме, где не был обнаружен референсный аллель) необходима, так как клинический эффект имеют не только обнаруженные вариации нуклеотидной последовательности, но и их отсутствие.
Отсутствие ALT аллеля в таких позициях генома не позволяет определить тип генетической вариации, для которой был обнаружен только референсный (REF) аллель. Запись генотипов для таких случаев усложняется необходимостью использовать источник информации о возможных аллелях для данной вариации и не покрывается данным руководством. Если потенциально вы будете использовать данное руководство и скрипт create_23andme.sh для конвертации VCF файла, полученного после полногеномного секвенирования в Атлас, сконвертированный файл не будет содержать референсные гомозиготные генотипы, так как скрипт create_23andme.sh явным образом фильтрует такие записи для исключения ошибок при формировании записей для инсерций и делеций.
Для того, чтобы скрипт create_23andme.sh все же выдавал референсные гомозиготные генотипы, вам необходимо заменить в нем содержимое строк 25–28
...
if [ "$ALT" == "." ] || [[ "$ALT" == *"*"* ]]
then
continue
fi
...на
...
if [[ "$ALT" == *"*"* ]]
then
continue
fi
if [ "$ALT" == "." ]
then
echo -e "$RSIDt$CHRt$POSt$REF$REF"
fi
...
Эта замена позволит выводить в stdout записи с гомозиготными референсными генотипами. Необходимо иметь в виду, что такие записи для инсерций и делеций будут некорректны, так как допустимые аллели в используемом формате для инсерций и делеций — это I и D, а скрипт будет использовать аллели A, G, T или C. Чтобы правильно выводить данные для инсерций и делеций, необходимо заранее знать о том, какой тип вариации свойственен данной позиции генома, в которой не был обнаружен ALT аллель. Эту информацию можно получить путем анализа ALT аллеля при его наличии (уже реализовано в create_23andme.sh) или использованием внешней базы данных, например, dbSNP (нет в create_23andme.sh).
Для того, чтобы получить отчет Promethease по полному VCF файлу полногеномного секвенирования в Атлас, можно загрузить в Promethease собственно сам VCF файл, однако нужно иметь ввиду, что размер предоставляемого Атлас сжатого VCF файла — около 8 гигабайт, тогда как Promethease позволяет загружать файлы не более 4 гигабайт. Описание решений этой проблемы доступно по ссылке. Еще одно решение заключается в разделении VCF файла на несколько частей (меньше 4 гигабайт каждая) и загрузке каждой в качестве дополнительного файла в меню загрузки данных Promethease.
Третье задание конкурса
Загрузите сконвертированные данные каждого из 12 образцов тестового датасета, который вы отфильтровали по списку вариаций в первой задаче, в Promethease и составьте таблицу соответствия идентификатор образца — определенная системой интерпретации Promethease группа крови AB0/Rh (Rh — Резус-фактор). Группы крови, определенные вероятностно и записанные с приставкой «prob» в отчете Promethease, запишите без приставки. Неопределенные значения запишите как unknown (Резус-фактор для unknown групп крови по-прежнему необходимо записать, если он определен). Пример представлен в Таблице 1.
Конвертация VCF в используемый выше формат в предложенной реализации сильно упрощена, но требует значительного количества времени. Для оптимизации вы можете написать скрипт с циклом, который автоматически будет выполнять генерацию этих данных, итерируя по набору идентификаторов. Можно сделать несколько таких скриптов и каждому передать разные наборы идентификаторов образцов для параллельного выполнения, однако количество параллельно запущенных скриптов не должно превышать количество ЦПУ вашего компьютера/виртуальной машины. Хорошее описание создания таких циклов доступно по ссылке. При работе на Яндекс.Облаке вы можете при необходимости создать еще одну виртуальную машину с бо́льшим количеством виртуальных ЦПУ, что позволит пропорционально сократить время на выполнение задачи.
Это последняя задача из нашего цикла. Ответы присылайте на почту wgs@atlas.ru до 26 декабря до 23:59. Правильные ответы и имена победителей опубликуем 28 декабря. Победитель получит тест Полный геном, а второе и третье места — генетический тест «Атлас». Также будут специальные призы от Яндекс.Облако. Бывшие и настоящие сотрудники Атласа в конкурсе не участвуют 😉


